Версія даної теми для друку
Натисніть сюди для перегляду даної теми у оригінальному форматі
Розподілені обчислення в Україні _ Медико-біологічні (завершені проекти) _ DrugDiscovery@Home alpha
Автор: ReMMeR Apr 22 2009, 16:28

Проект "DrugDiscovery@Home"
----------------------------------------------------------------------------------------------------------
- http://drugdiscoveryathome.com/
- http://boinc.drugdiscoveryathome.com/
- http://boinc.drugdiscoveryathome.com/team_members.php?teamid=494&sort_by=total_credit&offset=0
- http://boinc.drugdiscoveryathome.com/server_status.php
- http://stats.free-dc.org/stats.php?page=proj&proj=ddh
- http://stats.free-dc.org/stats.php?page=team&proj=ddh&team=494
ТОП-20 участников:

----------------------------------------------------------------------------------------------------------
Дата основания команды - 22.04.2009 Капитан - ReMMeR
----------------------------------------------------------------------------------------------------------
Для присоединения к команде Украины:
1. Загрузите http://boinc.berkeley.edu/download.php (Если его у Вас еще нет!)
2. Перейдите в "расширенный вид"
3. Выберите сервис ---> добавить проект
4. Введите адрес проекта http://boinc.drugdiscoveryathome.com/
5. Введите свои регистрационные данные.
6. Найдите нашу команду. Она называется Ukraine и адрес ее http://boinc.drugdiscoveryathome.com/team_members.php?teamid=494&sort_by=total_credit&offset=0 вы могли видеть выше.
7. Если есть доступные для загрузки задания Вы их получите и начнете расчеты.
----------------------------------------------------------------------------------------------------------
Новичкам: http://distributed.org.ua/index.php?go=Pages&in=view&id=170, как поставить и настроить BOINC-менеджер
----------------------------------------------------------------------------------------------------------
Полезная информация:
Для идентификации пользователя в BOINC могут служить 2 вещи:
1) пара e-mail/пароль
2) межпроектный идентификационный ID (Cross-project ID) - 32значное шестнадцатиричное число.
Если Вы пожелаете подключится ещё и к другому BOINC-проекту, то помните: чтобы не плодить новых аккаунтов при подключении к новому проекту или команде, нужно обязательно везде регистрироваться с одним и тем же Именем и EMAIL. если при регистрации в проекте указать другой e-mail , BOINC создаст новый аккаунт с тем же именем! В этом случае рекомендуется зайти во все ваши аккаунты и во все проекты и где надо поменять емейл на нужный. Через некоторое время ваши аккаунты сольются в один с одним cross-project-id.
----------------------------------------------------------------------------------------------------------
О проекте:
Drug Discovery at Home (в пер. с англ., найди лекарство дома) — российский биомедицинский проект распределенных вычислений, основанный на платформе BOINC. Научные цели проекта DrugDiscovery@Home (DD@Home) связаны с исследованиями фолдинга белков, рака, старения, стволовых клеток, а также с поиском новых лекарственных средств от ряда заболеваний. Проект пока не имеет формальных отношений ни с одной фармацевтической компанией или академическим учреждением, а развивается на энтузиазме и за счет смешанной российско-американской группы разработчиков.
В настоящий момент проводится предварительное альфа-тестирование серверной части проекта и расчетного клиента DrugDiscovery@Home, основанного на таких известных пакетах специализированного ПО как GROMACS (симуляция молекулярной динамики биологических молекул) и Autodock (молекулярный докинг). Желающие принять участие в альфа-тестировании или помочь в техническом развитии проекта, могут обратиться лично к Андрею Воронкову — научному сотруднику МГУ и главному куратору DrugDiscovery@Home.
Ссылки по теме:
Текст взят из : http://distributed.ru/wiki/pro:drugdiscovery © Arbalet
Автор: ReMMeR Apr 22 2009, 16:35
Пока что только по инвайтам, тозже обещают полный паблик.
Автор: kornq Apr 22 2009, 22:28
Тут есть на русском про проэкт - http://distributed.ru/wiki/pro:drugdiscovery
Автор: Rilian Apr 22 2009, 22:37
дайте инвайте![]() !!
!!
Автор: Rilian Apr 22 2009, 22:46
послал емейл админу проекта, чтобы выдал инвайте
Автор: -=Vzhik=- Apr 23 2009, 05:36
Да-да, мне бы тоже инвайт, чтобы с Ralph@Home уйти. пока ферма живая.
Автор: Rilian Apr 23 2009, 07:09
методом перебора (с первого раза) нашел инвайте. пишите, выдам в личке ![]()
Автор: Rilian Apr 23 2009, 07:21
User of the day
Profile rilian
I crunch for Ukraine
на маках И linux x64 пока считать нельзя
Thu 23 Apr 08:21:22 2009 DrugDiscovery [error] File autodock_1.302_i686-apple-darwin has wrong size: expected 125168, got 425376
Thu 23 Apr 08:21:22 2009 DrugDiscovery [error] Checksum or signature error for autodock_1.302_i686-apple-darwin
Автор: Rilian Apr 23 2009, 09:26
На винде тоже не считается
23.04.2009 10:23:36 DrugDiscovery Computation for task fzd2_25450_chemdiv_5408-3417_1240444995_1 finished
Автор: Death Apr 23 2009, 09:59
+1
я UoD )))))
Автор: (_KoDAk_) Apr 23 2009, 11:09
я тепер Я
+ этого проекта нет еще на фришниках)
Автор: YuRi Apr 23 2009, 11:18
Rilian, Death, (_KoDAk_), Они каждого вновь зарегистрированного юзера делают UoD (до регистрации следующего ![]() )
)
Rilian, Это такая серия заданий с ашыпками (fzd2_25450_chemdiv_бла_бла_бла). Есть другая (ХХХХ_1zd2_бла_бла_бла), та считается нормально.
На Е4400 ~4-5 минут, дают 0,7-1 очко за задание.
Автор: Death Apr 23 2009, 11:58
БоКу отписал. на фришниках должна скоро появиться.
Автор: (_KoDAk_) Apr 23 2009, 13:49
23.04.2009 14:47:59 DrugDiscovery [error] Can't rename output file fzd2_5_1240453555_1_0 to projects/boinc.drugdiscoveryathome.com/fzd2_5_1240453555_1_0: Error 2
Автор: Rilian Apr 23 2009, 15:00
Rilian, Death, (_KoDAk_), Они каждого вновь зарегистрированного юзера делают UoD (до регистрации следующего
Rilian, Это такая серия заданий с ашыпками (fzd2_25450_chemdiv_бла_бла_бла). Есть другая (ХХХХ_1zd2_бла_бла_бла), та считается нормально.
На Е4400 ~4-5 минут, дают 0,7-1 очко за задание.
скока жаб fdz2 надо убить чтобы начали выдаваться 1zd2 ?
Автор: (_KoDAk_) Apr 23 2009, 18:15
кучу всего он закачивает
Приєднані зображення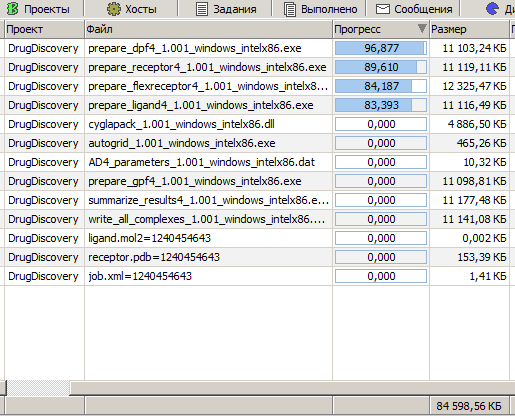
Автор: Rilian Apr 23 2009, 18:24
скока жаб fdz2 надо убить чтобы начали выдаваться 1zd2 ?
выдалось несколько штук
Автор: (_KoDAk_) Apr 23 2009, 19:52
убил уже много fdz2 но без толку (
и что-то на квад они неохотно лезут а на одноядерник налетают как мухи (
Автор: YuRi Apr 23 2009, 20:51
На Е4400 ~4-5 минут, дают 0,7-1 очко за задание.
У мну вчера вечером как пошлО качать эти fdz2... Штук 200 накачало, пока не запретил прием. Утром глянул - все с ошибками на первой же секунде и среди них штук 5-6 нормально посчитанных 1zd2.
Автор: (_KoDAk_) Apr 24 2009, 00:13
автар проекта сказал что через пару дней поймет вчем порблема
Автор: Rilian Apr 27 2009, 09:41
http://stats.free-dc.org/stats.php?page=proj&proj=ddh
Украина на 2м месте
2 российских команды в Топ-4
ура! ![]()
Автор: T0lsty Apr 27 2009, 10:32
и заданий нет
Автор: Rilian Apr 27 2009, 11:30
Скорее всего раздали очки за прошлые error-нутые ВЮ
Автор: Death Apr 27 2009, 11:34
http://stats.free-dc.org/stats.php?page=proj&proj=ddh
Overall
Team Total Credit
1. Russia 5,528
2. Ukraine 2,331
Хм. Давайте приколемся ))))))))
Автор: Rilian Apr 28 2009, 10:27
кому инвайте? пишите сюда
Автор: Death Apr 28 2009, 10:46
28.04.2009 11:22:26 DrugDiscovery Starting fzd2_78_ga10_1240897818_3
28.04.2009 11:22:47 DrugDiscovery Starting task fzd2_78_ga10_1240897818_3 using autodock_mgl version 103
28.04.2009 11:40:44 DrugDiscovery [error] Can't rename output file fzd2_78_ga10_1240897818_3_0 to projects/boinc.drugdiscoveryathome.com/fzd2_78_ga10_1240897818_3_0: Error 2
28.04.2009 11:41:00 DrugDiscovery Computation for task fzd2_78_ga10_1240897818_3 finished
28.04.2009 11:41:42 DrugDiscovery Sending scheduler request: To fetch work.
28.04.2009 11:41:42 DrugDiscovery Reporting 1 completed tasks, requesting new tasks
28.04.2009 11:41:46 DrugDiscovery Scheduler request completed: got 0 new tasks
28.04.2009 11:41:46 DrugDiscovery Message from server: (Project has no jobs available)
сцуко 18 минут в *опу.
23.04.2009 11:22 10 564 AD4_parameters_1.001_windows_intelx86.dat
28.04.2009 03:57 10 564 AD4_parameters_1.003_windows_intelx86.dat
23.04.2009 10:55 448 321 autodock_1.001_windows_intelx86.exe
23.04.2009 10:55 487 424 autodock_1.002_windows_intelx86.exe
28.04.2009 03:58 448 321 autodock_1.003_windows_intelx86.exe
28.04.2009 03:57 487 424 autodock_mgl_1.003_windows_intelx86.exe
23.04.2009 11:22 476 425 autogrid_1.001_windows_intelx86.exe
28.04.2009 03:57 476 425 autogrid_1.003_windows_intelx86.exe
23.04.2009 10:55 591 360 cygblas_1.001_windows_intelx86.dll
28.04.2009 03:57 591 360 cygblas_1.003_windows_intelx86.dll
23.04.2009 11:21 5 003 776 cyglapack_1.001_windows_intelx86.dll
28.04.2009 03:58 5 003 776 cyglapack_1.003_windows_intelx86.dll
23.04.2009 10:57 1 873 811 cygwin1_1.001_windows_intelx86.dll
28.04.2009 03:57 1 873 811 cygwin1_1.003_windows_intelx86.dll
28.04.2009 11:45 3 012 job.xml=1240908289
28.04.2009 11:45 2 639 ligand.mol2=1240908289
28.04.2009 03:57 1 079 make_sitecustomize_1.003_windows_intelx86.py
28.04.2009 04:00 21 495 334 MGLToolsPckgs_1.003_windows_intelx86.zip
23.04.2009 11:10 11 369 719 prepare_dpf4_1.001_windows_intelx86.exe
23.04.2009 11:51 12 621 281 prepare_flexreceptor4_1.001_windows_intelx86.exe
23.04.2009 11:34 11 365 182 prepare_gpf4_1.001_windows_intelx86.exe
23.04.2009 11:15 11 383 289 prepare_ligand4_1.001_windows_intelx86.exe
23.04.2009 11:24 11 385 964 prepare_receptor4_1.001_windows_intelx86.exe
28.04.2009 03:57 2 117 632 python25_1.003_windows_intelx86.dll
28.04.2009 11:45 157 055 receptor.pdb=1240908289
23.04.2009 11:36 11 445 740 summarize_results4_1.001_windows_intelx86.exe
23.04.2009 10:54 167 936 unzip_1.001_windows_intelx86.exe
28.04.2009 03:58 167 936 unzip_1.003_windows_intelx86.exe
23.04.2009 11:47 11 408 466 write_all_complexes_1.001_windows_intelx86.exe
23.04.2009 10:54 135 168 zip_1.001_windows_intelx86.exe
28.04.2009 03:58 135 168 zip_1.003_windows_intelx86.exe
32 файлов 123 145 962 байт
123 метра.
Автор: Rilian Apr 28 2009, 10:48
За еррорнутые ВЮ тоже пока выдают очки, так что не переживай. Тем более как бе альфа-тест. Все ок
Автор: Death Apr 28 2009, 12:00
да я собственно пофиксил его.
28.04.2009 11:54:16 DrugDiscovery Starting fzd2_623_ga10_1240908289_0
28.04.2009 11:54:22 DrugDiscovery Starting task fzd2_623_ga10_1240908289_0 using autodock_mgl version 103
28.04.2009 12:08:13 DrugDiscovery Restarting task fzd2_623_ga10_1240908289_0 using autodock_mgl version 103
28.04.2009 12:27:33 DrugDiscovery Restarting task fzd2_623_ga10_1240908289_0 using autodock_mgl version 103
28.04.2009 12:58:25 DrugDiscovery Computation for task fzd2_623_ga10_1240908289_0 finished
28.04.2009 12:58:39 DrugDiscovery Sending scheduler request: To fetch work.
28.04.2009 12:58:39 DrugDiscovery Requesting new tasks
28.04.2009 12:58:41 DrugDiscovery Started upload of fzd2_623_ga10_1240908289_0_0
28.04.2009 12:58:49 DrugDiscovery Finished upload of fzd2_623_ga10_1240908289_0_0
28.04.2009 12:58:51 DrugDiscovery Scheduler request completed: got 0 new tasks
28.04.2009 12:58:51 DrugDiscovery Message from server: (Project has no jobs available)
хуле переживать-то )))))))
Автор: Death Apr 28 2009, 15:02
Task ID
click for details
Show names Work unit ID
click for details Sent Time reported
or deadline
explain Status CPU time (sec) claimed credit granted credit
45215 12274 28 Apr 2009 12:23:58 UTC 5 May 2009 12:23:58 UTC In progress --- --- ---
45156 12227 28 Apr 2009 11:10:32 UTC 28 Apr 2009 12:19:28 UTC Completed and validated 827.28 0.88 0.72
45141 12258 28 Apr 2009 10:54:16 UTC 28 Apr 2009 11:10:32 UTC Completed and validated 682.19 0.73 0.73
45055 12235 28 Apr 2009 8:45:06 UTC 28 Apr 2009 9:59:25 UTC Completed and validated 851.63 0.91 0.81
44872 12189 28 Apr 2009 5:55:10 UTC 28 Apr 2009 8:41:35 UTC Error while computing 124.02 0.13 ---
44653 12129 28 Apr 2009 2:06:18 UTC 28 Apr 2009 5:31:47 UTC Completed and validated 688.58 0.73 0.73
44594 12116 28 Apr 2009 0:56:43 UTC 28 Apr 2009 5:30:28 UTC Completed and validated 689.06 0.73 0.73
44328 12066 27 Apr 2009 21:51:46 UTC 28 Apr 2009 0:56:43 UTC Error while computing 24.17 0.03 ---
43953 12001 27 Apr 2009 18:27:53 UTC 27 Apr 2009 21:31:13 UTC Error while computing 0.00 0.00 ---
43650 11951 27 Apr 2009 14:58:09 UTC 27 Apr 2009 18:26:37 UTC Error while computing 0.00 0.00 ---
43177 11873 27 Apr 2009 11:30:48 UTC 27 Apr 2009 14:58:09 UTC Error while computing 0.00 0.00 ---
42999 11842 27 Apr 2009 9:39:34 UTC 27 Apr 2009 11:29:30 UTC Error while computing 0.00 0.00 ---
31568 9624 24 Apr 2009 14:30:39 UTC 25 Apr 2009 14:46:27 UTC Error while computing 1.11 0.00 ---
31298 9580 24 Apr 2009 13:38:08 UTC 24 Apr 2009 14:30:39 UTC Error while computing 1.16 0.00 ---
31071 8779 24 Apr 2009 3:39:24 UTC 24 Apr 2009 6:07:56 UTC Error while computing 1.39 0.00 ---
30916 9522 23 Apr 2009 21:06:42 UTC 24 Apr 2009 0:20:04 UTC Error while computing 0.59 0.00 ---
30460 9437 23 Apr 2009 17:59:05 UTC 23 Apr 2009 21:06:41 UTC Error while computing 0.42 0.00 ---
29417 9415 23 Apr 2009 14:54:12 UTC 23 Apr 2009 17:59:05 UTC Error while computing 0.44 0.00 ---
27449 9351 23 Apr 2009 10:25:04 UTC 23 Apr 2009 14:54:12 UTC Error while computing 1.13 0.00 ---
27272 9295 23 Apr 2009 9:16:31 UTC 23 Apr 2009 9:18:01 UTC Error while computing 1.06 0.00 ---
шото мало очей. голиме селероне.
Автор: Death Apr 28 2009, 15:11
ладно, потроллил и хватит.
http://boinc.drugdiscoveryathome.com/forum_thread.php?id=4&nowrap=true#43
скучно. больше щитать не буду. да и очков мало.
http://boinc.drugdiscoveryathome.com/profile_rate.php?userid=514&vote=recommend
ВСЕ ЗАХОДИМ!
Автор: Death Apr 29 2009, 21:41
http://boinc.drugdiscoveryathome.com/forum_thread.php?id=4
проект уже начинает доставлять.
юсовец не знает олбанского а туда же...
Автор: Rilian May 2 2009, 12:37
Обращайтесь в личку, выдам инвайт ![]()
кстати на mac os уже работает без ошибок
Автор: Rilian May 2 2009, 12:43
@death нафига троллить на проектном форуме?
Автор: Rilian May 2 2009, 12:49
Currently we are running some screening on both a proprietary database and the open NCI Plated compounds of some 600K compounds. At the moment I cannot comment on the advantages of running these simulations. At the very least we can use these benchmarks to compare with other analysis.
Here is a link to the current protein we are analyzing.
http://www.rcsb.org/pdb/explore/explore.do?structureId=3B7E
Проект начал анализировать докинг белка который встречается в штамме "свиного гриппа" H1N1
Автор: (_KoDAk_) May 2 2009, 16:02
так вот оно что, это эпидемия всего лиШш промо акция для этого проекта) ![]()
Автор: Rilian May 3 2009, 20:58
to Rilian <*****@gmail.com>
date Sun, May 3, 2009 at 7:10 PM
subject Re: DrugDiscovery@Home
Пока временно не принимаем новых тестеров. Теперь ждите открытого бета теста.
Автор: Death May 3 2009, 21:03
Rilian, а где ж троллить-то???
ВУ нету (((
Автор: T0lsty May 4 2009, 10:43
какието задния большие . на c2q 3.4 уже 10 часов считается.. 75 % ровно и не двигается .
Автор: T0lsty May 4 2009, 20:22
пля уже 18 часов .. и теже 75 % ...
Автор: Rilian May 5 2009, 09:55
пля уже 18 часов .. и теже 75 % ...
http://boinc.drugdiscoveryathome.com/forum_thread.php?id=2
пишут что все что больше часа недосчитывается можно прерывать
Автор: Rilian May 7 2009, 23:43
У меня снова есть инвайт код ![]()
пишите в личку
Автор: (_KoDAk_) May 10 2009, 16:06
1 SETI.USA 9 2,347 33,299 United States None
2 SETI.Germany 13 1,559 18,565 Germany None
3 Free-DC 2 1,481 18,191 International None
4 Ukraine 6 951 15,864 Ukraine None
5 Russia 14 725 14,882 Russia National
6 The Planetary Society 1 1,081 13,990 International None
Автор: Rilian May 12 2009, 12:26
Database/file status
State #
Results ready to send 167,692
Results in progress 104,433
каждое задание по 30 сек
пишите в личку, есть инвайт!
Автор: (_KoDAk_) May 12 2009, 18:41
а сколько балов за это 30сек заданияе ?
Автор: Rilian May 12 2009, 23:39
а сколько балов за это 30сек заданияе ?
по разному
http://boinc.drugdiscoveryathome.com/results.php?userid=514&offset=60&show_names=0&state=3
Автор: Death May 13 2009, 10:21
13.05.2009 11:19:50 DrugDiscovery Reporting 343 completed tasks, not requesting new tasks
Автор: Rilian May 28 2009, 16:31
ояебу результаты проекта Gromacs 0.07 - по 55МБ!
Автор: YuRi May 28 2009, 21:26
У мну - 61,27. ![]()
Уже третий день не могу отправить то что посчиталось. Остальные абортированы сервером.
Пожалуй, я на этот проект забью. Жалко только потерянные сутки... ((
Автор: Rilian May 28 2009, 21:30
да, одмины пишут чтобы сделали тем вю аборт
Автор: YuRi May 28 2009, 21:48
Ну уж нет уж! Я их считал - пускай теперь принимают. ))
Может в следующий раз будут чем-то думать прежде чем раздавать всякую фигню.
Автор: Rilian May 28 2009, 21:57
проект - альфа, им по статусу положено фигню раздавать! ![]()
Автор: T0lsty Jun 5 2009, 12:16
кони
05.06.2009 13:12:00 DrugDiscovery Started upload of run_1244161897938054867_2_0
05.06.2009 13:12:01 DrugDiscovery [error] Error reported by file upload server: Server is out of disk space
объем для аплоада 37 мб/ву
Автор: ReMMeR Jun 5 2009, 12:43
ОЛОЛОЛО
Автор: T0lsty Jun 14 2009, 20:52
около 5к пендинга превратилось в 0 .
почти все задания - Completed, can't validate.
причем считалось на неразогнанном кваде ..
шо ж праймгрид покажет щас ..
Автор: T0lsty Jun 14 2009, 21:28
ЭтаЖесть .
суко испугались .
почти на всех заданиях Completed, can't validate. но очки дали !! а было по нулям .
Автор: Rilian Jun 14 2009, 21:34
они мониторят наш форум! ![]()
Автор: gow Jun 15 2009, 15:07
у кого есть инвайт прошу поделится
Автор: Rilian Jun 15 2009, 21:37
поделился.
пишите в личку или сюда, кто хоче инвайт
Автор: T0lsty Jun 24 2009, 12:30
издеваюцца
24.06.2009 13:31:32 DrugDiscovery Message from server: No work sent
24.06.2009 13:31:32 DrugDiscovery Message from server: (reached daily quota of 2 tasks)
этопри том что задания вываливаются с ошибкой сразуже.
Автор: T0lsty Jul 15 2009, 10:23
есть много заданий , правда коротких .
кто хочет/может поддержите команду .
Автор: Tamagoch Jul 17 2009, 12:25
T0lsty,
нужен инвайт?
Автор: T0lsty Jul 17 2009, 14:27
вроди да .
если кому нужен инвайт - просите Rilian, у него есть .
Автор: Tamagoch Jul 17 2009, 14:30
Рилиан в аську не отвечает, а я уезжаю от фермы и уже не успею стартануть сегодня полную мощность...
2rilian:
дай инвайте ![]()
Автор: T0lsty Jul 17 2009, 15:17
мож Remmer знает
Автор: ReMMeR Jul 17 2009, 21:21
Инвайта нету, а письмо с инвайтом не могу найти ![]()
Автор: (_KoDAk_) Jul 18 2009, 07:50
July 14, 2009
Happy Bastille Day! We are now looking at GPU integration for GROMACS. We may need a little help with this integration. Here is a thread I started which includes links to related code. There is a msvc solution for building gromacs and there are various pre-compiled libraries for integrating cuda called OpenMM, read more http://boinc.drugdiscoveryathome.com/forum_thread.php?id=84
July 17, 2009
We are working on several things, resolving problems with certain ligands, experimenting with GPUs and studying the feasability of optimizing gromacs for PS3s for our project.
. I am also planning another BOINC Meetup. This time a social gathering on the US National Mall to watch Close Encounters of the 3rd Kind. Bring your SETI Shirts http://opensource.meetup.com/84/ некая социальная сеть )
Автор: (_KoDAk_) Jul 18 2009, 10:50
есть два инвайта
третий уже дал Tamagoch, у)
Автор: Tamagoch Jul 18 2009, 11:19
(_KoDAk_),
спасибо ![]()
Автор: Rilian Jul 27 2009, 13:17
Кому дать инвайт код? Пишите сюда.
В проекте сейчас очень много маленьких заданий. Считаются по 5 минут
Автор: vitalidze1 Jul 27 2009, 14:44
Мужики, підкиньте інвайт в ЛС, посчитаємо
Автор: vitalidze1 Jul 27 2009, 15:26
Мужики, підкиньте інвайт в ЛС, посчитаємо
Нових юзерів не приатаччують до клієнта, покищо.
Автор: Death Jul 28 2009, 11:30
они нопейчасле шо пока это альфа они не хотят толпы юзеров которые кранчат без фидбека.
Автор: Rilian Jul 29 2009, 10:23
Накранчил 10000
пс: Jack Schultz скажет когда они откроют создание аккаунтов
Автор: (_KoDAk_) Jul 29 2009, 12:12
а ты на сайт зайти можеш ? под своим логином?
если да то значит и клиента можно подключить
создай рукими
account_boinc.drugdiscoveryathome.com.xml
сосвоим авторизиционным кодом и пробуй
Автор: Rilian Jul 29 2009, 12:30
а ты на сайт зайти можеш ? под своим логином?
если да то значит и клиента можно подключить
создай рукими
account_boinc.drugdiscoveryathome.com.xml
сосвоим авторизиционным кодом и пробуй
имеется ввиду "нельзя создать аккаунт"
пс: юзайте правильную терминологию
Автор: (_KoDAk_) Jul 29 2009, 12:39
но если судить по самому себе (по РВ в целом )
то еще ни разу я ни написал того что они не знали(им кто-от это уже написал) или то го что хотели узнать (они этого и не планируют делать)
вот такая картина (
Автор: Rilian Aug 2 2009, 23:38
Сайт оффлайн ..
Автор: Rilian Aug 6 2009, 08:47
Базу восстановили, но она откатилась на 2 недели назад. ![]()
собсно, это еще раз подтверждает необходимость ежедневных бэкапов или настройки полной немедленной репликации
Автор: (_KoDAk_) Aug 6 2009, 18:54
потери таковы
1 T0lsty -131,276.1 -->6,339.1
2 rilian -8,932.2 -->716.8
3 UA_ReMMeR -12,552.1 -->628.4
4 Vzhik -18,334.4 -->415.5
5 (_KoDAk_) -3,647.9 -->202.5
6 Death -406.1 -->35.8
Автор: Rilian Aug 6 2009, 19:50
мдямс.
я кстати мыло Джеку Шульцу отправил с просьбой восстановиь кредиты вручную. Посмотрим что ответит
Автор: ReMMeR Aug 6 2009, 22:27
Неприятно конечно.
За Толстого обидно.
Автор: T0lsty Aug 7 2009, 08:33
да капец .. херячил всем что было .. и вот тебе на ..
Автор: Rilian Aug 7 2009, 09:21
восстановим, не переживайте. надо тока время
Автор: Rilian Aug 7 2009, 22:02
Восстановили очки! ![]()
![]()
![]()
![]()
Автор: Rilian Aug 11 2009, 09:50
DrugDiscovery@Home - Project Up
We are in the process of restoring user data
![]()
но
11.08.2009 10:45:20 DrugDiscovery Started download of autodock_mgl_1.022_windows_intelx86.exe
11.08.2009 10:45:22 DrugDiscovery Giving up on download of autodock_mgl_1.022_windows_intelx86.exe: file not found
Автор: Rilian Aug 11 2009, 14:35
Загрузка вроде уже пашет. Пробуйте кто зарегистрирован ![]()
обновили автодок до 1.024
Автор: (_KoDAk_) Aug 11 2009, 15:04
я что-то про пустил чего они не грузят проц ?
Автор: Rilian Aug 11 2009, 17:32
кранчим с (_KoDAk_) одну ВЮ на пару ![]()
http://boinc.drugdiscoveryathome.com/workunit.php?wuid=37286
грузят 100%
Автор: (_KoDAk_) Aug 11 2009, 23:13
уже нет
видать задания какоето время заняты ЧЕМТО
что не грузит проц(
Автор: Rilian Aug 12 2009, 07:39
У меня грузят и на win32 и на mac
Автор: Tamagoch Aug 14 2009, 12:25
у меня так сразу было... 2-3 минуты что-то делает какими-то своими утилитами (распаковывает что ли) и не грузит проц, потом запускается автодок и минут 20-25 считает
Автор: T0lsty Aug 14 2009, 14:22
как раз в момент распаковки проц не юзается почти , но комп тупит огого...
а когда куча мелких заданий - это ппц .
Автор: (_KoDAk_) Aug 26 2009, 15:44
а вот теперь задания по 8 и больше часов и ктому же все с ошибками
Автор: Rilian Aug 26 2009, 22:27
2009-08-26: Our project is back online. We now have a workflow to further analyze docking results using molecular dynamics. We are also on the verge of providing GPU support. Our project needs its volunteers to come back. Your credits can be restored. Just provide us your username, authenticator and email address. We also have acocunt creation temporarily enabled so you can register. -Jack
Пишут, что открыли рекистрацию и проекту нужно больше компьютеров
Автор: T0lsty Sep 19 2009, 19:38
Кодаг - Пользователь Дня ![]()
Автор: Rilian Oct 5 2009, 21:23
2009-10-05: We are improving the progress bar for our apps. This is especially important for mdrun where we want to run simulations for several days. With a progress bar that updates every 100 steps of a 5 million step simulation, a cruncher should be more confident that the simulation is running properly if they see th progress bar updating over the course of 5 days. In addition, checkpointing is already a feature native to this app, so if you pause, you should be able to return to the same point in the simulation. -Jack
пишут что ВЮ будут по 5 дней ![]()
Автор: T0lsty Oct 5 2009, 21:47
у них крайности ..
то 9-10 сек .. то 5 дней ..
нах такое нада
Автор: (_KoDAk_) Oct 5 2009, 22:39
не дружественный проект однозначно
T0lsty, прав крайностей им не занимать
Автор: Rilian Oct 5 2009, 22:49
это альфа проект, ошибки или не стабильне время ВЮ могут быть.
Автор: Rilian Oct 12 2009, 21:47
початился с админом проекта. позже напишу новости
и да если у когото есть вопросы - задавайте, я форвардю
Автор: Rilian Oct 14 2009, 21:52
Проект переезжает на более мощный сервер (на тот же хостинг что и проект Hydrogen@home)
Те длинные 5-дневные задания использовались для тестирования, в том числе и возможности разбивать большие задания на более мелкие. В будущем задания будут меньшего размера.
Также в проекте пока много проблем с программой mdrun (MD = molecular dynamics)
Также ведутся работы над более точным прогрессбаром в MGL Tools/ Autodock
Также ведутся работы над исследовательской стратегией проекта (то есть что считать).
Также возможно через какое-то время будут какието публикации о прогрессе проекта DD@H.
Автор: Peret Nov 14 2009, 23:46
Открыта регистрация в проекте.
Только ведет он себя, мягко говоря, странно.
загрузил 450 ![]() заданий дедлейн до 19 числа
заданий дедлейн до 19 числа ![]() пришлось все отменять.
пришлось все отменять.
Автор: Rilian Nov 28 2009, 21:57
Jack Shultz:
I could talk a little more in specifics but to be brief, there are topics that I have a hard time understanding and I need more help from theoretical chemists.
Right now I'm developing a reverse screening workflow. Our collaborator at the University of Oslo has a set of compounds he does not know what they are good for, so we want to go through all know protein structures to find what are good scores.
Автор: Rilian Dec 15 2009, 19:29
MDRUN app is working very well on Windows and 64-bit Linux. There is a little problem on startup for 32-bit Linux where the wrapper fails to execute. It should be fixed in a few days. Otherwise the project is looking spectacular!
Автор: Tamagoch Dec 26 2009, 09:33
удалили мой аккаунт, хотят инвайт за регистрацию.... стоит ли? ![]()
зы. Кодак - юзер дня! ![]()
Автор: Rilian Dec 26 2009, 13:38
удалили мой аккаунт, хотят инвайт за регистрацию.... стоит ли?
когда ?
инвайт могу достать
Автор: Tamagoch Dec 26 2009, 23:58
не смог зайти на сайт под своим мылом, пишет что нет такого
а я есть в стате команды? у меня были очки, судя по записям polarseti
от инвайта не откажусь.... снова
попробую не отключаться от проекта, чтобы помнили
Автор: Rilian Dec 27 2009, 00:42
Tamagoch,
http://boinc.drugdiscoveryathome.com/show_user.php?userid=731
вышли мне в ЛС емейл с твоего аккаунта
Автор: Death Feb 15 2011, 23:01
свежачок от админа проекта.
ну что, протянем руку помощи тянем руку помощи младшим братьям?
========
В общем с учетом того, что Джек занялся активно подработками проекту нужен девелопер. Платить могу только из личных денег, поэтому либо Джек же и будет если согласится на относительно скромные ставки или еще кого то поискать придется, ну или просто на всякий случай будем искать для страховки второго девелопера.
В общем нужен специалист для работы с проектом Drugdiscovery@home:
- Управление сервером BOINC, управление заданиями для распределенных вычислений, исправление багов
- Кросс-платформенная компиляция исходного когда разных приложений с открытым кодом
- Исправление и написание управляющих скриптов PHP, C++, perl
А до тех пор проект будет в некой спящей фазе...лично я бросать его не собираюсь, но тк я отвечал за программную часть, сосбтвенно используемые приложения, то теперь придется всю серверную BOINC часть осваивать с нуля практически в свободное от основное работы и семьи время.
Автор: Alien Feb 16 2011, 01:36
оо, мне интересен этот проект, с точки зрения развития...
помните, мы типа такого же хотели сделать =).
если он нуждается, я бы ему мог бы помочь, как биолог.. чуть опыта работы в автодоке есть.. в громаксе больше.
Death, я думаю можно помочь, на условии, что проект будет официально при участии украинцев и задания могут отправлять тоже украинцы. Будет справедливо, если он будет требовать сертификаты личности по принадлежности к тем или иным гос. учреждениям. У каждого нашего ученого, кто занимается вычислениями такое есть. Так что со своей стороны мы можем гарантировать, что от нас не будут ставить проекты люди с улицы.
https://ca.ugrid.org/valids.php
Автор: Death Feb 16 2011, 11:17
хочется также услышать Рильяна - он рулил кажется боинк сервером + знает ПХП и может компилить аппы.
Реммер тоже призывается в тред.
Автор: ReMMeR Feb 16 2011, 11:40
Death, по настройке именно сервера - могу помочь если что.
Но не боинка. Ни разу не настраивал.
Рилян настраивал Боинк.
Автор: Rilian Feb 16 2011, 12:44
насколько я помню Джек хотел сделать коммерческий проект и предлагать его можности лабам ? Почему бы им не объединиться с RNAWorld, раз они преследуют те же самые цели?
Автор: Death Feb 16 2011, 13:18
как я понял джек пошол зарабатывать бабло и на ДД забил
Автор: Death Feb 17 2011, 14:38
пригласил Андрея сюда.
надо уточнить какой объём трудозатрат потребуется и есть ли принципиальное согласие Рема, Рила и Эла ))))
Автор: bestdrug Feb 19 2011, 13:09
пригласил Андрея сюда.
надо уточнить какой объём трудозатрат потребуется и есть ли принципиальное согласие Рема, Рила и Эла ))))
На данный момент в рабочий процесс внедрены следующие расчетные программы: GROMACS, Autodock.
Текущие ключевые задачи:
1. Нужно внедрить дополнительно две утилиты – фильтрацию баз соединений по физико химическим и фрагментным параметрам (это надо для отбрасывания заведомо токсичных соединений и тп). Софт с открытым кодом наиболее интересный подобран. Надо сделать кросс платформенную компиляцию, но ключевой момент – внедрить в рабочий процесс (чекпойнты там сделать и тп) и отловить как можно больше багов приводящих к сбоям на стороне клеинтов.
2. Из-за проблем с дисковым прсотранством, а также наверное каких то технический проблем (мы должны это обсудить с Джеком, но он ушел в подполье...просто дисковое пространство то вроде увеличили..) GROMACS сохраняет только последний фрагмент траектории. Т.ее. допустим считаем молекулярную динамику в течении 1 наносекунды, делим на 10 частей, каждая например по 100 пикосекунд. Надо решить проблему записи файлов на локальный диск
3. Внедрение в рабочий процесс скрипта MM PBSA для GROMACS. Здесь мне еще надо потестировать скрипт оффлайн тк он еще вообще в принципе не доработан. Было бы неплохо конечно подклчить программиста разбирающегося еще и в молекулярной динамике сюда.
Два первых пункта ключевые для того чтобы сделать первый полноценный испытания проекта с возможностью опубликования. Дальше публикацию надо использоавть для получения грантов. Третий пункт значительно уркасит рабочий процесс и может способствовать увеличению точности расчетов. Собственно Джек почти что доделал до конца первые два пункта , но после потери работы у него отношение к волонтерской деятельности сильно изменилось и хотя доделать осталось немного пока не очень получается его подключить.
4. Внедрение GPU версий. Над этим Джек сейчас работает.
5. Внедрение разных мелких и занятных вспомогательных утилит – типа распознавания структур в патентах с целью создания открытой базы патнетов с химическим поиском (аналог freepatents online, который сейчас стал платным к сожалению).
6. Внедрение софта для прогнощирования свойств ADME.
7. Софт для генерации новых структур лигандов методом de novo с пропусканием их потом через фильтры ADME, а также фармакофорные модели.
8. Свободный софт для адекватного создания фармакофорных моделей- такой найти надо сначала.
Исправление багов и увеличение количества усешных посчитанны
Автор: Alien Feb 19 2011, 17:14
1- для каких целей вы используете громакс, для получения кластера структур, в эквиваленте гибкого рецептора? Возможно в случае фильтрации с помощью комбинированных вычислительных процедур, типа MM-PBSA, кластер уже неактуально?
2- софт для отбора лигандов вроде существует, мне кажется это можно и до запуска проекта сделать автору (правда я не уверен, что в течении нескольких дней все может сделать). Обратите внимание на pipeline pilot. Какие утилиты используете вы?
3- то что меньше наносекунд - это пикосекунды, шаг записи траектории выставляется в файле md.mdp.
4- какой метод, для оценочной функции свободной энергии будете использовать?
5- касательно исследуемых образцов, публикаций и грантов, здесь не все так плохо... к примеру M. tuberculosis, актуально и есть наработки.
6- пусть джек пока не тратит время на ГПУ, функционал там обрезан, если хотите точности пока упустите этот вопрос и сконцентрируется на других.
7- каким методом будете определять биологически-активную конформацию?
Автор: bestdrug Feb 21 2011, 00:16
1- для каких целей вы используете громакс, для получения кластера структур, в эквиваленте гибкого рецептора? Возможно в случае фильтрации с помощью комбинированных вычислительных процедур, типа MM-PBSA, кластер уже неактуально?
2- софт для отбора лигандов вроде существует, мне кажется это можно и до запуска проекта сделать автору (правда я не уверен, что в течении нескольких дней все может сделать). Обратите внимание на pipeline pilot. Какие утилиты используете вы?
3- то что меньше наносекунд - это пикосекунды, шаг записи траектории выставляется в файле md.mdp.
4- какой метод, для оценочной функции свободной энергии будете использовать?
5- касательно исследуемых образцов, публикаций и грантов, здесь не все так плохо... к примеру M. tuberculosis, актуально и есть наработки.
6- пусть джек пока не тратит время на ГПУ, функционал там обрезан, если хотите точности пока упустите этот вопрос и сконцентрируется на других.
7- каким методом будете определять биологически-активную конформацию?
Спасибо за интересные вопросы.
1. Да, действительно одна из задач GROMACs в рабочем процессе - получение ансамблей структур, кластеризация и отбор репрезентативных или средних (на данный момент ориентируемся на репрезентативные плюс локальная минимизация) с последующим докингом (пока гибкий но тут тозе ансамбли интересная альтернатива). Однако это один из этапов. Есть тн модель релаксированного комплекса - те когда ансамбли берутся для уже известного лиганда, это упрощает задачу. Если речь идет о рецепторе где отсутствуют лиганды то смоделировать индуцированное соответствие таким образом намного сложнее в случае если конформация сайта связывания в активной и неактивной форме сильно отличаются (что имеет место быть для большинства подобных задач). Таким образом молекулярная динамика все таки актуальна для моделирования индуцированного соответствия и конформационного перехода в белках. Другой вопрос в том сколько времени моделируемого - длины траектории понадобится в разных случаях. Это можно обсудить отдельно. Второй момент - это растовритель. При ансамблях и докинге так по хорошему его надо убирать т.к. положение молекул воды не зная положения лиганда просчитать сложно и обратно, т.е да можно делать докинг с замещением воды, но с учетом опять таки динамических условий в реальности -измнений конформационных, а таке проблем с оценочными функциями в докинге, в общем молекулярная динамика представляется наиболее эффективным способом учета растворителя в явном виде. Кроме того, есть желание попробовать вообще говоря посмотреть корреляцию стабильности комплекса белок-лиганд при молдинамике с аффинностью - pKi например. А MMPBSA таки в данном случае не фильтровочная процедура, а процедура для ранжирования итоговых структур. Ну допустим сделали мы докинг отобрали средневзвешано по кластерам 100 лигандов с наилучими значениями усредненных оценочных функций, ввели в молдинамику после 10 наносекунд например 10 комплексов остались стабильными с сдвигом лиганда относительно сайта связывания например менее 3 ангстрем. Тогда дальше мы эти лиганды берем и просто как дополнительную процедуру для ранжирования используем MM PBSA. Можно и пожалуй нужно испольовать и другие доплнительные, например консенсусные и индивидуальные оценочные функции и т.п.
2. Если говорить про фильтрацию и генерацию 3D координат, то в общем то можно использовать локально уже сейчас, проблем нет. Потенциально рабочий процесс должен быть применен по отношению к большим базам данных, например виртуальнымх химическим прсотранствам с более чем 1 млрд соединений. Там очень много соединений, которые не пройдут фильтры и эти фильтры можно подстроить так чтобы проходило например только 10% реглируя жесткость критериев. На данном этапе есть на выбор несколько разных утилит. Ключевое требование - софт должен быть с открытым кодом. В целом софт можно уже использовать сейчас и я думаю так и сделать. К сожалению есть проблема с 3D генераторами - кроме OMEGA2 пока не видел генераторов, которые бы не портили бы ароматические системы - гнут циклы и соответственно смешщают все заместители и т.п. Это очень серьезно. Тот который мы рассматриваем сейчас - Frog2 один из наиболее приятных, но тоже страдает этой проблемой. Если знаете нормальный 3D генератор - дайте знать. Пока что для небольшой выборки соединений проблему удается решить разбиением ансамбля конформаций лигандов и выбором репрезентативных структур там такой проблемы не наблюдалось пока. А кластеризация для базы данных уже затратное дело. Pipeline pilot от Accelrys это коммерческая программа. Не могу использовать коммерческий софт не от МГУ не от исследовательского иснтиута где сейчас работаю (Норвегия) т.к. проект независимый и мы должны все сконструировать либо на свободном софте либо на своих мощностях. Насчет пилота для своей текущей работы рассматриваю как один из вариантов без привязки к DD@H.
В целом так вообще сейчас думаю что можно только с траекториями разобраться и можно сделать работу, хотя генерация 3х мерных координат все таки несколько напрягает, с неадекватными трехмерными структурами докинг начинать не хочется, а использование omega2 в проекте невозможно долгосрочно, только если 1 раз для статьи чисто академической и то если лицензию дадут.
3. Конечно пикосекунды, опечатался, сорри
4. Автодоковская оценочная функция и MM PBSA как писалось выше но для энтальпийной части, а для энтропийной если будем то нормальные моды соответственно. Какие то дополнительные оценочные функции не знаю нужны или нет, но как писал выше рассматриваем скорее всего консенсус из всего что есть не по коммерческой лицензии и по отдельности тоже можно смотреть. У меня есть небольшой список, который надо доплнять.
5. Проблем с выбором биомишени, проверкой, сотруднчиества с биологчиескими группами в принципе особых нет. Тематики интересные и интересные биомишени и лиганды есть. Нас интересует регенеративная медицина и сигнальные пути стволовых клеток и противораковая терапия. Но в целом если проект заработает то академической коллаборации мы конечно будем рады и открыты для нее.
6. Нет Джек тратит, потому что функционал есть неурезанный. Молекулярная динамика с явно заданным растоврителем сейчас используется и для GROMACS и в NAMD. А может и еще где. Работ уже много интересных, по GROMACS - команда Folding@home.
7. Скорее это так по большому счету ансамбль конформаций и отчасти поэтому такой цели нет. В лучшем случае...построить фармакофорную модель трехмерную соответственно. Но для этого еще надо соответстующую утилиту и еще вопрос по каким принципам строить. Если есть что то типа динамической фармакофорной модели это вообще было бы идеально пока не слышал такого
Автор: Alien Feb 21 2011, 01:20
бгалодарен за детальные ответы. попробую прокомментировать и помочь.
1- "Другой вопрос в том сколько времени моделируемого - длины траектории понадобится в разных случаях. Это можно обсудить отдельно."
Это достаточно сложный и очень важный момент. Конечно все зависит от процентного количества гибких участков в макромолекуле, но стоит рассматривать релаксационный период более 50 нс, в эквиваленте силового поля громос, ориентировочно для белка массой ~60-120 кДа. К примеру по исследованиям 5 годичной давности, когда проводили динамику тирРС человека, считалось, что релаксация наступает уже на 5 нс, но когда я начал использовать грид-инфраструктуру и мощные кластера, выяснилось то, о чем писал выше.
Исходя из этих данных, подготавливать проект и создавать кластер лучше локально на мощном кластере, ибо принцип лейки (1-2 ядра на задачу от волонтера) будет неприемлем из-за низкой скорости выполнения проекта.
Касательно воды, тоже согласен, очень важно и проблематично. Ведь много реакций катализа в активном центре происходит при участии молекул воды и от куда брать их координаты. В мире пока ориентируются на связи экспериментальных данных и проводят докинг направленно.
Но тут далеко не всем везет.
Исходя из того, что ресурсов много, можно использовать более точные оценочные функции, по идее, энергетика несильно долго считается.
2- "1 млрд соединений" это с учетом по сотне конформаций для каждого лиганда? То их вроде всего 8 млн.
по моим данным, лучше связки OMEGA + catalyst, пока что не придумали =). Есть ряд успешных проектов, которые были подтверждены экспериментально, базируясь на этом методе. Видел еще альтернативу, но нужно поискать в статьях, они заведомо хуже.
"с неадекватными трехмерными структурами докинг начинать не хочется, а использование omega2 в проекте невозможно долгосрочно, только если 1 раз для статьи чисто академической и то если лицензию дадут."
полностью согласен, сперва нужно убедиться что со структурой все ок. касательно лицензии, ну может на разные отделы или НИИ оформлять? =)) Не будет же сотни публикаций, в которых будет фигурировать ОМЕГА, можно и ссылаться, что было посчитано в рамках предыдущего.
3- Речь не про шаг записи, который вообще в фемтосекундах, а про куски траектории, т.к. по 1 наносекунде мы пользователям не посылаем.
эм, есть шаг расчета динамики, а есть там же и шаг записи хтс и трр, ниже. возможно кто-то удалил строчку, которой регулируют.
1 микросекунду на 1-2 ядра - это самоубийство считать методами БОИНК =))). Лучше использовать мощные кластера Норвегии, которых достаточно.
мы тут с ребятами как-то обсуждали и пришли к выводу, что задачи ФХ то может и интересно считать в БОИНК, но в докинге то рецепторы побольше будут и проводить расчеты более 1 нс, я сомневаюсь что есть смысл. ведь тут следующий фрейм зависит от предыдущего.
6- возможно с целью докинга, ограничения незначительны, но тут частично описано http://www.gromacs.org/Downloads/Installation_Instructions/Gromacs_on_GPUs?highlight=gpu
Просто коллеги биофизики экспериментировали с опенмм по расчету энергии, результаты удивили даже разработчиков, которые так и не дали внятных ответов и просили ждать дальнейшего развития. Вот и мы у себя считаем, нужно чуть подождать, нормального кода. Такие расчеты только еще дальше в дебри уведут. Но мы работаем с гпу акселерацией, в применении для анализа траекторий. Там сильно сложной математики нет и переживать не стоит.
7- из того что я знаю, фармакофорную модель строят за принципом суперпозиции к РСА или ЯМР, с кат-офом не более 2.5 А.
В целом очень рад, у вас действительно серьезный подход, только буду рад, в случае вашего активного развития. =))
Автор: bestdrug Feb 28 2011, 12:08
На всякий случай - дискуссия очень интересная, я обязательно напишу ответ. Так если совсем вкратце.
1. Действительно разброс может быть довольно большой в зависимости от размеров белка, гибкости и т.п. Нас интересует вопрос на данном этапе не столько о стабильности структуры белка и ее реклаксации, что безусловно важно и наверное даже должно быть может и первым шагом, а вопрос о стабильности лиганд-белкового комплекса. В целом идеально было бы протестировать это на данных РСА с хорошим разрешением. А так...ну есть проект Folding@home они имитируют фолдинг траекториями по 1 нс. У них есть задача изучения траектории, там работает чисто статистика. Можем ли мы пойти тем же путом и моделировать структуру, а не только имитировать фолдинг? Для этого должны быть некие критерии, там свободная энергия, укладка и т.п. Т.е. если мы запускаем 100-200 процессов по 1 нс у нас есть в каких то случаях шанс получить релаксированную структуру. Впорос в том как ее отобрать. Насчет кластера согласен, но очень интересно было бы сделать проект независимым от внешних расчетных ресурсов.
2. 1 млрд это виртуальные библиотеки несинтезированных, даже если по 1 й конфрмации на лиганд (для гибкого докинга достаточно), для жесткого еще больше. Насчет наилучшей эффективности ОМЕГА не спорю, ну там ооочень большие проблемы с лицензиями, все очень жестко - только академическим группам для академических работ и никаких распределенных вычислений иначе цена лицензии от 30 до 50 тыс долл в год. Кроме того, очень хотелось бы найти софт с открытым кодом, имхо это вообще наиболее так сказать морально оправданное направление в компьютерной разработке лекарств - софт с открытым кодом тк издержки на разработку лекарств и так огромны. В общем мы ориентируемсмя на самый эффективный софт из того что есть с открытым кодом, это единственное что нам подходит по лицензии как и любому проекту распределенных волонтерских вычислений.
3.Окей есть шаг расчета, шаг записи и т.п.
Folding@home для имитации фолдинга использует распределенные вычисления. В целом не вижу проблемы, но давйте обсудим. Сейчас пока основная задача - попробовать оценить стабильность комплексов белок-лиганд и сделать исходные соответственно данные для анализа методом MM-PBSA. Допустим
10 000 вокрклюнитов по 100 пикосекунд, 1000 пользователей, 1 сутки на воркюнит...вполне можно сделать, но это очень очень грубая прикидка сейчас, ориентировочная...Опять же две разные задачи - оптимизация структуры белка и изучение стабильности лиганд-белковых взаимодействий.
Давайте чуть подробнее здесь попробуем подискутировать, может даже я почитаю побольше публикаций на эту тему. И докинг лиганда, те взаимодействие с белком и фолдинг - оба процесса статистические, значит можно использовать одинаковые методы для их имитации. Разница только в том, что в фолдинге мы знаем конечною структуру и нам простон адо понять траекторию, а в случае лиганд-блековых взаимодействий или например оптимизации структуры белка - нет. Но...фолдинг то начинается у нас с денатурированного белка, а оптимизация структуры и изучение лиганд-белкового комплекса в общем то с какой то уже достаточно близкой к нативной структуры. Т.е. есть и недостатки при расчете БОИНком, но и преимущества для таких задач получается тоже есть.
6. Насчет OpenMM может быть сейчас и не совсем та версия, которая отвечает полностью нашим задачам. Но мы сейчас на той тсадии чтобы научится вообще с этим кодом работать и использовать его в расчетах, на тренировочной стадии можно сказать. А так в принципе можно придумать задачи адекватные и для той версии, которая есть. Хоть что нибудь если-бы в GPU реализовано было бы...уже хорошо.
7. Ну это фармакофорная модель на основе РСА комплекса лиганд-белок. Это в идеальном случае. А так можно строить по чему и как угодно и не факт что не будет работать ![]() Но в данном случае рассматриваются разные варианты. Идеальный - описанный Вами РСА комплекса белок-лиганд. Еще вариант - набор биологически активных лигандов, например в LigandScout делается генерация конформаций, они кластеризуются отбираются наиболее вероятные для каждого из лигандов и строится модель фармакофорная. По своему опыту скажу, что конечно в зависимости от выборки лигандов можно получить довольно разные модели и чем химическое разнообразие больше, тем в целом больше есть шанс получения верной модели. В общем при отсутствии РСА биомишени это скорее вынужденный подход, чем наиболее эффективный. Но тем не менее он тоже, как мне представляется, имеет право на существование.
Но в данном случае рассматриваются разные варианты. Идеальный - описанный Вами РСА комплекса белок-лиганд. Еще вариант - набор биологически активных лигандов, например в LigandScout делается генерация конформаций, они кластеризуются отбираются наиболее вероятные для каждого из лигандов и строится модель фармакофорная. По своему опыту скажу, что конечно в зависимости от выборки лигандов можно получить довольно разные модели и чем химическое разнообразие больше, тем в целом больше есть шанс получения верной модели. В общем при отсутствии РСА биомишени это скорее вынужденный подход, чем наиболее эффективный. Но тем не менее он тоже, как мне представляется, имеет право на существование.
Большое спасибо за интересные вопросы и комментарии! Извиняюсь за задержку с ответами, буду стараться отвечать и дальше.
На всякий случай мой личный контакт - av@drugdiscoveryathome.com
Автор: Rilian Feb 28 2011, 12:44
TODO: вынести проект в отдельный форум. Вынести научное обсуждение в отдельный топик
Автор: Alien Mar 1 2011, 02:27
Спасибо за ответ.
предлагаю обращаться к друг-другу на ты, мы приблизительно одинакого возраста =)
ну если из соображений, что изначально рецептор был получен после кластеризации релаксированного участка траектории, то конечно, может 1 нс и хватит.
Первый концептуальный вопрос который возникает, после прочтения этой фразы
Динамику комплексов вы себе представляете классической механикой? В идеале бы сделать по методу MM\QM, при расчете активного центра и лиганда. PC Gamess вроде бесплатен. Но я как-то вел беседу с квантовиками, они сказали при участии более 10 а.о. уже будут серьезные тормоза.
А тут, может я чего-то недопонял, но кажется в корне неправильное понимание -
Это ты имел ввиду, что в динамике стремится конформация к той что мы видим после РСА или ЯМР? Ну как бы это "условный" теоретический эталон, хоть и экспериментальный. Я читал что последние исследования говорят о том, что РСА предоставляет низкоэнергетические конформации, а биоактивные обладают чуть выше энергией и чуть отличаются. Тоже самое касается и ЯМР, там зависит от растворителя (гидрофобный или гидрофильный). Я понимаю, что лучшего ориентира нет, но и воспринимать как последнюю инстанцию не стоит, как по мне).
И так, в целом я теперь понимаю, что вы планируете делать. Осталось конструктивно описать то, что уже сделано и что осталось сделать.
Так же можно выделить то, что можно отложить на будущее, на дальнейшее развитие. К примеру, гпу клиент я бы отложил - это не приоритетная задача.
Возможно, стоит нарисовать схему алгоритма и на ней отобразить то, что актуально для разработки, чтоб здешние ребята, кто разбирается в программировании, смогли помочь.
P.S. А пробовали ли на кафедру биоинформатики МГУ обращаться за помощью?
Автор: Death Mar 21 2011, 11:56
пурумпумпу
есть ву
Автор: Alien Apr 17 2011, 23:43
Мы с Андреем сейчас по имейлу переписываемся, но чтоб были в курсу, я тут нашел книжечку с тезисами.. и увидел аналогичный проект англичан.
http://enterthegrid.com/ThirdAlmereGridWorkshop/ProceedingsThirdAlmereGridWorkshop.pdf
ст. 23-27.
Автор: Rilian May 26 2013, 14:24
вы не поверите но проект начинает работу снова!
http://boinc.drugdiscoveryathome.com/
2 Feb 2013
Change in administration
For the next couple of months I'll be taking over administrating this project. Having neigh on no experience with the BOINC back-end, I'm looking forward to it, if only for the added experience.
As the first thing, I have updated the forum software and merged the forums.
Then hacked the database to add the news forum. The script that should've done this didn't work. I am now trying to fix it so the news actually shows on the front page, not just in the 'old news' section.
There's no work as of yet. I'm busy trying to figure out how to get a Java application working with the new BOINC wrapper. But for this wrapper to work, we need more up-to-date BOINC server software, so guess what's next on the To-Do list?
19 May 2013
Back
As far as I saw, it was a virus injection in the Drupal code that the front page uses. It's taken all this time to take it down as it ran on a server I had no access to.
The next thing to do is ask Google to come check our sanity any further. And see what we want to do with the Drupal front page. if anyone has more Drupal knowledge than me, PM me. Of course, if you know how to make a fancy HTML page, your help is also welcome.
Автор: ArsenEverlast Jan 23 2017, 21:25
в проекті знову зявилися завдання, на моєму i7-6700K рахуються 200-500 секунд, за кожне завдання дають 3 очка
Автор: tawejesin Feb 5 2017, 03:02
Задания все валят и валят. А у нас на форуме по этому проекту тишина, проект вообще в завершенные перенесли
Автор: re_SET Feb 5 2017, 23:23
Кстати да. Два человека педалят. А хочется бооольшееее...
Автор: Death Feb 6 2017, 22:07
ни описания ресерча, ни кто стоит за етим - фсбшное говно какоето небось
Автор: tawejesin Feb 7 2017, 16:20
ни описания ресерча, ни кто стоит за етим - фсбшное говно какоето небось
Подтверждаю. Инфа 146%
А список команды Украина надо передать в СБУ. Наградят. Орден дадут. Орден Иуды называется.
Омерика з нами!
Автор: Dromage Feb 8 2017, 10:24
Death, tawejesin. Ой, ребята не начинайте - прошу вас.
За себя могу сказать что не считаю, потому что разорвать свои отнюдь не бесконечные ресурсы на все проекты невозможно. А у меня и так за все время считались 25 ныне действующих проектов + 17 уже завершенных. Итого 42. Ведь хочется всем помочь, везде успеть...
Сейчас приоритет у меня на Прайм, Энштейн и WCG (кроме проектов не требующих процессорного времени). По одному проекту на каждое из 3-х направлений. А так как DrugDiscovery@Home - двоюродный родственник WCG, то ему моего внимания, к сожалению, не хватает.
Автор: tawejesin Feb 14 2017, 15:49
ни описания ресерча, ни кто стоит за етим - фсбшное говно какоето небось
Ну да, мутный тип какой-то. Описание проекта не дает. Похоже, грант замутил и создает видимость работы. Нашел только http://www.interface.ru/home.asp?artId=38015, Сколково, рай при жизни! Чубайс, много денег, дай, дай, дай, и очень много, и прочий негатив...
Но из принципа смысла нет считать чего-то Омериканцам, все равно наебут.
Хотел братьям-хохлам помочь посчитать их проект nanosurf, но проект оказался еще более мутный, чем DrugDiscovery.
Автор: Death Feb 22 2017, 00:50
Воронков Андрей Эдуардович, Руководитель
Баринов Владимир Игоревич, Программист
Джон Шульц, CIO, главный разработчик
Гайфуллин Булат (Интерфейс), Анализ и обработка больших массивов данных
Автор: tawejesin Apr 5 2017, 13:42
Недолго ждать пришлось, Воронков с поляками чего-то делит, шкуру неубитого медведя. Похоже, деньгами запахло.
https://boinc.drugdiscoveryathome.com/forum_thread.php?id=2091#4830
Валю на другой проект
Приєднані зображення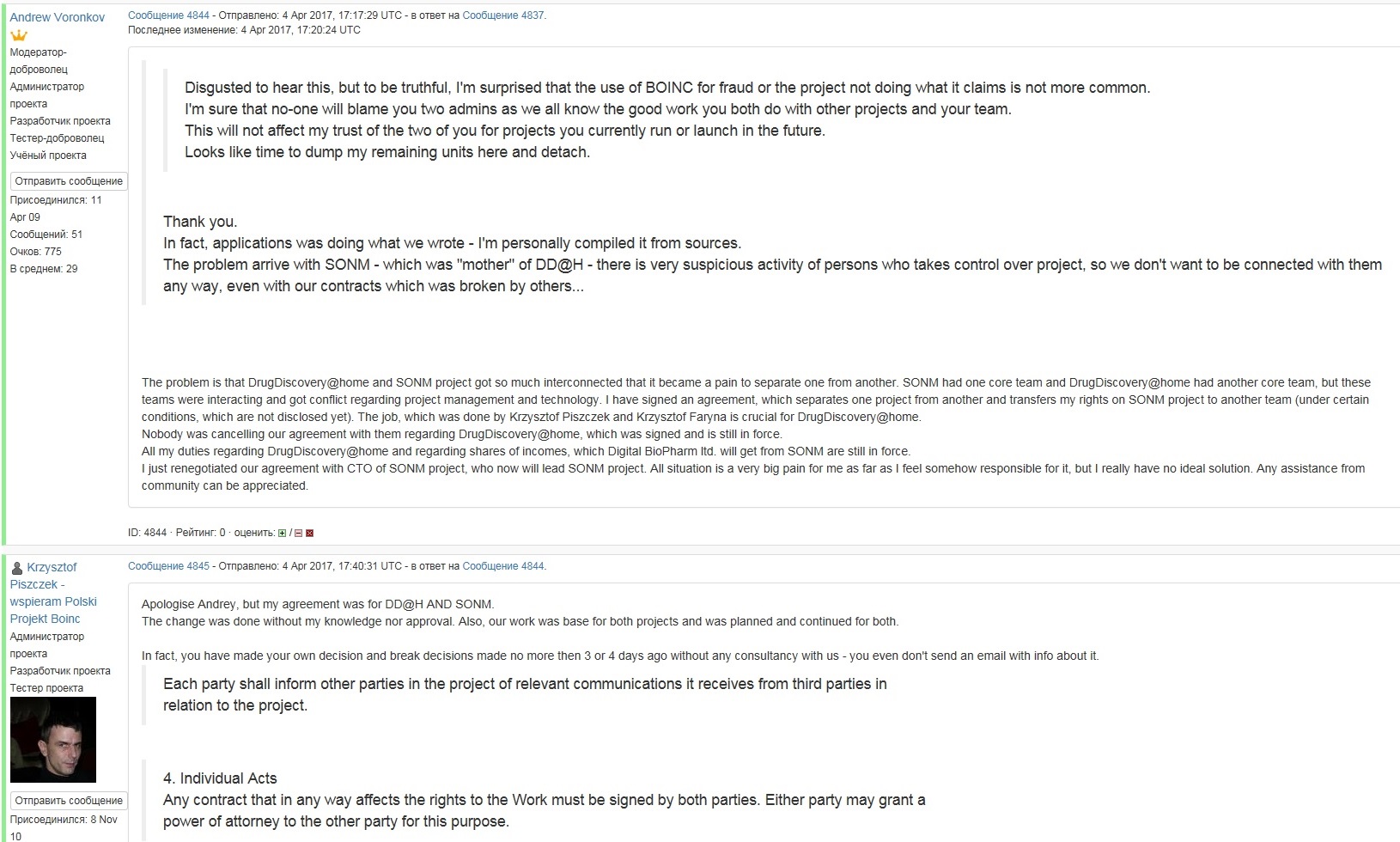
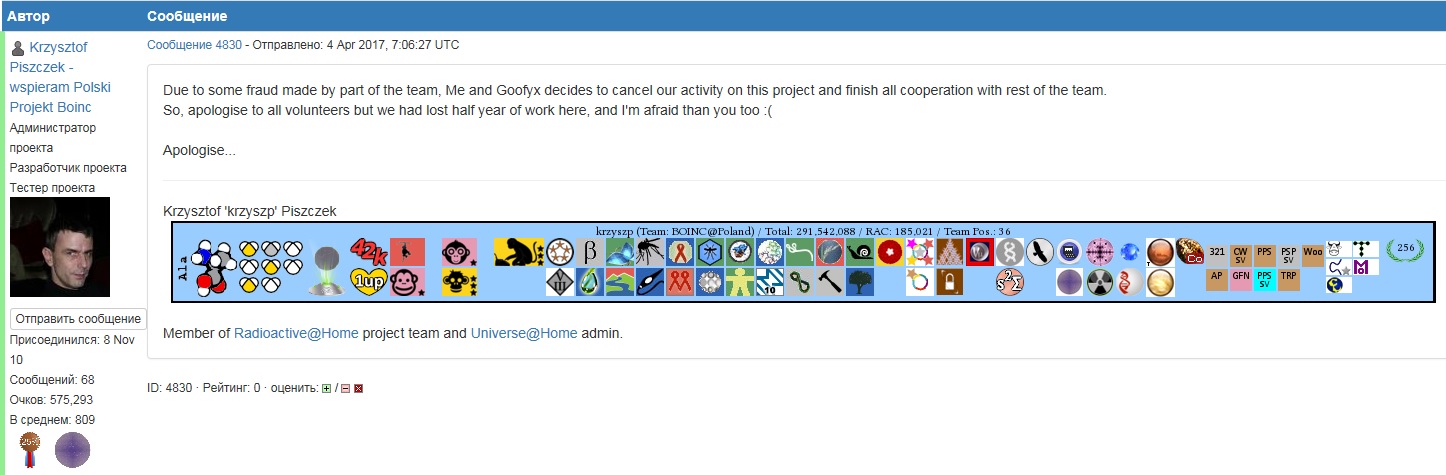
Автор: ArsenEverlast Apr 6 2017, 09:44
хотів добити медальку за 100к очків, набрав тасків на 4 компах, нарахував 3,5к тасків і проект здох( могли б хоча б дати можливість злити готові завдання
Автор: Vasyan_Nyasha Oct 30 2017, 16:21
Для тех кто ищет медико-биологический проект с cpu+gpu - аот он!!!
Проект активен и запустил недавно версию для gpu.
Автор: tawejesin Dec 15 2017, 17:28
Для тех кто ищет медико-биологический проект с cpu+gpu - аот он
Проект активен и запустил недавно версию для gpu.
Поляки денег подали, апнуть тему решил?
Нет там никакого ГПУ.
За кого топишь?
Автор: Vasyan_Nyasha Dec 17 2017, 14:51
https://boinc.drugdiscoveryathome.com/forum_thread.php?id=2108&postid=5001
Автор: tawejesin Dec 19 2017, 09:46
Ничего не нашел
Приєднані зображення
Автор: Vasyan_Nyasha Dec 19 2017, 10:56
Я писал в конце октября. Сейчас середина декабря...
И посмотрите в https://boinc.drugdiscoveryathome.com/apps.php
Видите Gromacs?
В версии написано (cuda23), что как бы намекает.
Сейчас заданий нет, но на момент написания были.
P.S
А вас братья славяне подкупили?
Автор: tawejesin Dec 19 2017, 16:56
Слушай, пионэр. Вот в каждой теме без тебя не обошлось... Хватить чушь писать. Иди лучше уроки учи.
Родители знают, чем ты занимаешься?
Invision Power Board
© Invision Power Services
