Привіт Гість ( Вхід | Реєстрація )
| Rilian |
 Jun 11 2008, 15:33 Jun 11 2008, 15:33
Пост
#1
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
 Human Proteome Folding Project Phase 2 Официальные результаты проекта Активные эксперименты Human Microbiome Project - официальный сайт http://homepages.nyu.edu/~rb133/wcg/thread_2010_03_10.html Как присоединиться читайте в главном топике World Community Grid Proteins are essential to living beings. Just about everything in the human body involves or is made out of proteins. What are proteins? Proteins are large molecules that are made of long chains of smaller molecules called amino acids. While there are only 20 different kinds of amino acids that make up all proteins, sometimes hundreds of them make up a single protein. Adding to the complexity, proteins typically do not stay as long chains. As soon as the chain of amino acids is built, the chain folds and tangles up into a more compact and particular shape that lets it conduct specific and necessary functions within the human body. Proteins fold because the different amino acids like to stick to each other following certain rules. Imagine that amino acids are pop-beads of 20 different colors. The pop-beads are sticky, but sticky in such a way that only certain combinations of colors can stick together. This makes the amino acid chains fold in a particular way that creates proteins that are useful to the human body. Human cells have mechanisms to help the proteins fold properly and, equally important, mechanisms to get rid of improperly folded proteins. How do proteins relate to human genes? The collection of all of the human genes is known as "the human genome." Depending on how the genes are counted, there are over 30,000 genes in the human genome. Each gene, which is a section of a long chain known as DNA, dictates how to build the chain of amino acids for one of the 30,000 proteins. In recent years, scientists were able to map the sequence for each human gene. This means that we now know the sequence of amino acids in all of the human proteins. Thus, the human genome is directly related to the "human proteome," the collection of all human proteins. The protein mystery While researchers have learned a great deal about the human proteome, the functions of most of the proteins remain a mystery. The genes do not reveal exactly how the proteins will fold into their final shape, which is critical because that determines what a protein can do and what other proteins it can connect to or interact with. Proteins are like puzzle pieces. For example, muscle proteins connect to each other to form a muscle fiber. They join together in a specific manner because of their shape, as well as other factors relating to the shape. Everything that goes on in cells and in the body is very specifically controlled by the shape of the proteins that do or do not let proteins interlock with other proteins. For example, the proteins of a virus or bacteria may have particular shapes that enable it to break through the cell membrane, allowing it to infect the cell. The Human Proteome Folding Project Знания структуры белков позволит ученым понять как белки выполняют свои биологические функции, а также как болезни блокируют белки от выполнения необходимых функций для поддержания здоровых клеток The Human Proteome Folding Project will combine the power of millions of computers in a grid to help scientists understand how human proteins fold. The work to be done in this monumental task is shared across this grid, so that results can be achieved far sooner than would be possible with conventional supercomputers. With a greater understanding of protein structure, scientists can learn how diseases work and ultimately find cures for them. When your grid agent is running, it is folding an amino acid chain in various ways and evaluating how well each folding follows the specific rules of how specific amino acids stick together or not. As computers try millions of ways to fold the chains, they attempt to fold the protein in the same way that it actually folds in the human body. The best shapes identified for each protein are returned to the scientists for further study.  ----- Оказывается тут тоже юзается розетта (Show/Hide) График проекта  Це повідомлення відредагував Rilian: Feb 4 2011, 00:23 |
  |
Відповідей(45 - 59)
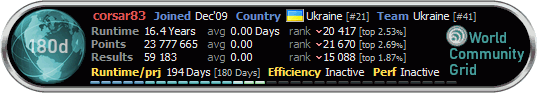
| corsar83 |
 Sep 27 2010, 09:20 Sep 27 2010, 09:20
Пост
#46
|
|
кранчер зі стажем       Група: Trusted Members Повідомлень: 426 З нами з: 28-January 10 Користувач №: 1 282 Стать: Чол Free-DC_CPID Парк машин: Pentium E6500 2,93Ghz, Phenom X6 1055T 2.8Ghz Gigabyte 5870OC(875/4800), Radeon 5750 |
блин что за фигня - задания считаются меньше минуты и выдает "Ошибка вычисления" (Show/Hide) то же самое и с Help Cure Muscular Dystrophy - Phase 2 Настраивай касперский (или у тебя другой антивирь -------------------- |
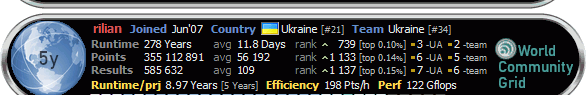
| Rilian |
 Sep 27 2010, 09:28 Sep 27 2010, 09:28
Пост
#47
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
Вроде все так и сделано, но не хочет. В списке киса вобще почему-то нету исполняющих по протеоме, не в довереных, не в ограничениях. По остальным проектам есть. А можно как-то сделать, чтоб по протеоме перегрузились заново все необходимые файлы с сайта? зайди в папку проекта wcg в data и все exe файлы добавь в "доверенные" "перезагрузка" проекта в этом случае бесполезна блин хоть убей всё облазил не могу найти эту папку и файлы. Куда оно его скачует в папке боинка нету. Всю XP облазил так и не нашёл. при запуске БОИНКа в первых строчках Messages есть этот путь -------------------- |
| tiss |
 Sep 27 2010, 09:33 Sep 27 2010, 09:33
Пост
#48
|
 Мега ранчер         Група: Trusted Members Повідомлень: 1 640 З нами з: 28-February 09 Користувач №: 952 Стать: Чол Free-DC_CPID |
при запуске БОИНКа в первых строчках Messages есть этот путь Типа так 09/27/10 10:06:53 Starting BOINC client version 6.10.45 for windows_x86_64 09/27/10 10:06:53 Config: report completed tasks immediately 09/27/10 10:06:53 log flags: file_xfer, sched_ops, task 09/27/10 10:06:53 Libraries: libcurl/7.19.7 OpenSSL/0.9.8l zlib/1.2.3 09/27/10 10:06:53 Running as a daemon 09/27/10 10:06:53 Data directory: C:\ProgramData\BOINC 09/27/10 10:06:53 Running under account boinc_master 09/27/10 10:06:54 Processor: 4 GenuineIntel Intel® Core™ i5 CPU 650 @ 3.20GHz [Family 6 Model 37 Stepping 2] 09/27/10 10:06:54 Processor: 256.00 KB cache --------------------  |
| Rilian |
 Sep 27 2010, 10:10 Sep 27 2010, 10:10
Пост
#49
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
Видимо пункт про антивирусы надо вписать в нашу стандартную "шапку" подключения к BOINC-проектам
-------------------- |
| corsar83 |
 Sep 27 2010, 10:42 Sep 27 2010, 10:42
Пост
#50
|
|
кранчер зі стажем       Група: Trusted Members Повідомлень: 426 З нами з: 28-January 10 Користувач №: 1 282 Стать: Чол Free-DC_CPID Парк машин: Pentium E6500 2,93Ghz, Phenom X6 1055T 2.8Ghz Gigabyte 5870OC(875/4800), Radeon 5750 |
Вроде все так и сделано, но не хочет. В списке киса вобще почему-то нету исполняющих по протеоме, не в довереных, не в ограничениях. По остальным проектам есть. А можно как-то сделать, чтоб по протеоме перегрузились заново все необходимые файлы с сайта? зайди в папку проекта wcg в data и все exe файлы добавь в "доверенные" "перезагрузка" проекта в этом случае бесполезна блин хоть убей всё облазил не могу найти эту папку и файлы. Куда оно его скачует в папке боинка нету. Всю XP облазил так и не нашёл. при запуске БОИНКа в первых строчках Messages есть этот путь Да вчера уже разобрался. Оказывается у протеомы исполняемый файл называется по хитрому я и не подумал вначале, что это он. Уже заработало -------------------- |
| Rilian |
 Sep 27 2010, 10:45 Sep 27 2010, 10:45
Пост
#51
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
Да, вообще-то в WCG в исполняемых файлах на windows нету букв .exe. Надо тоже это в шапку прописать..
-------------------- |
| corsar83 |
 Sep 27 2010, 10:54 Sep 27 2010, 10:54
Пост
#52
|
|
кранчер зі стажем       Група: Trusted Members Повідомлень: 426 З нами з: 28-January 10 Користувач №: 1 282 Стать: Чол Free-DC_CPID Парк машин: Pentium E6500 2,93Ghz, Phenom X6 1055T 2.8Ghz Gigabyte 5870OC(875/4800), Radeon 5750 |
Да, вообще-то в WCG в исполняемых файлах на windows нету букв .exe. Надо тоже это в шапку прописать.. Это да. Но в других проектах хоть названия такие же токо сокращенно. А по протеоме в каспере был файлик, точно не помню уже типа Client....(тут не помню)... и вспоминания про институт Парижа (или Нью Йорка )и еще чото (длинное название), вобще думал это рекламка какаето. Оказалось именно оно -------------------- |
| corsar83 |
 Sep 27 2010, 19:21 Sep 27 2010, 19:21
Пост
#53
|
|
кранчер зі стажем       Група: Trusted Members Повідомлень: 426 З нами з: 28-January 10 Користувач №: 1 282 Стать: Чол Free-DC_CPID Парк машин: Pentium E6500 2,93Ghz, Phenom X6 1055T 2.8Ghz Gigabyte 5870OC(875/4800), Radeon 5750 |
Это чо в протеоме каждое задание считается по 15 раз
-------------------- |
| Rilian |
 Sep 27 2010, 20:18 Sep 27 2010, 20:18
Пост
#54
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
corsar83, всегда так было. задания немного разные, на самом деле. подробнее на англ в официальном форуме..
-------------------- |
| Gelo |
 Sep 28 2010, 13:55 Sep 28 2010, 13:55
Пост
#55
|
 мрію про ферму...      Група: Trusted Members Повідомлень: 204 З нами з: 17-July 09 З: Дніпропетровськ Користувач №: 1 114 Стать: Чол Free-DC_CPID Парк машин: Microsoft Windows 7 Ultimate (64-bit), DualCore Intel Pentium E2160@ 3000 MHz, 2048 Гб - озу, ATI Radeon HD 5870(gpu 960Mhz), ATI Radeon HD 5770(gpu 960Mhz), 250 и 500 Гб винты. |
блин что за фигня - задания считаются меньше минуты и выдает "Ошибка вычисления" (Show/Hide) то же самое и с Help Cure Muscular Dystrophy - Phase 2 Настраивай касперский (или у тебя другой антивирь пользуюсь авастом, ставил в доверенные - один хрен. Помогло удаление-добавление проекта. ЗЫ: начались траблы с этим проектом после переустановки виндовса, до этого считалось нормально. -------------------- (Show/Hide)        |
| Tamagoch |
 Sep 28 2010, 15:55 Sep 28 2010, 15:55
Пост
#56
|
 Мультікранчер         Група: Trusted Members Повідомлень: 1 731 З нами з: 27-September 03 З: Бровари Користувач №: 18 Стать: Чол Free-DC_CPID Парк машин: Xeon 2690v2 (6x quiet mode), AMD Ryzen 5 3600 (6x no-HT), Intel i5 3rd gen (4x), а також все інше під рукою |
Да, вообще-то в WCG в исполняемых файлах на windows нету букв .exe что весьма кстати, если в офисе существует запрет на скачку исполняемых файлов и лень (а если правильно, то по соображениям безопасности не хочется) его отключать -------------------- (Show/Hide) |
| Rilian |
 Oct 21 2010, 16:51 Oct 21 2010, 16:51
Пост
#57
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
-------------------- |
| Rilian |
 Feb 3 2011, 16:16 Feb 3 2011, 16:16
Пост
#58
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
Долгожданный апдейт!
http://homepages.nyu.edu/~rb133/wcg/thread_2011_01_31.html HPF2 Update - January 2011 Greetings WCG Community, Happy new year! I have taken it upon myself to write a quick status update regarding the Human Proteome Folding project, in part to introduce myself and also to summarize a few of the tasks that lie ahead for us. As of early January, the Bonneau lab team working on the HPF project has undergone a slight change of staff. Patrick Winters, from whom you have heard in previous updates, has moved on to other pastures, and I have taken his place. My name is Duncan Penfold-Brown, and I am coming out of a previous research position in the application of high-powered computing (both Grid and Cloud) to high-energy physics and astronomy. I have a degree in computer science, and have in the past focused on distributed and self-organizing systems. I also have experience (and a great deal of interest) in bioinformatics, which I look forward to increasing in my work on this project. In short, I will be responsible for support and development of HPF projects and research. I am interested in pursuing a greater knowledge of proteomics - which seems to me like biological puzzle solving - and also the applications (medical, investigative) of the research we are completing together. The immediate tasks we are approaching are to work on improving our pre- and post-analysis tools, in order to get more data to the Grid, and to better interpret what comes out. Goals for the immediate future include continuing the incorporation of phylogenetic data and evolutionary analysis of protein domains into our analysis process in order to enhance our annotation of select unknown proteins. This incorporation will provide us with a better understanding of the function of unknown proteins, as we can more accurately identify evolutionarily similar structures and cross-examine their structure-function relationships. With additions to our analysis process and continued work, we will ultimately be improving the end data of our research. Speaking of data, here is a quick update of what is currently being turned over on the WCG: Currently, all protein data being folded is from the Human Microbiome Project (HMP - see their site at http://commonfund.nih.gov/hmp/), with a focus on microbes found in the human gut. As of late January, we have completed pre-analysis on the last of the data that we will be working on from the HMP (for now), and have dropped it off to be picked up by the grid (see codes 'oh' - 'ok' in the following table). We are now looking into new organisms - such as the malaria parasite Plasmodium Yoelii Yoelii (a model rodent malaria important for understanding the function of human malaria) - to analyze and send to the grid. The following table describes the data that has recently been or is being processed by the WCG: CODE Code Experiment Project/Organism Description Status oa 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Finished ob 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Finished oc 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Working... od 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Working... ... 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Working... og 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Working... oh 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Submitted oi 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Submitted oj 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Submitted ok 1169 Microbiome Novel Gastro-Intestinal proteins from the Human Microbiome Project Submitted Thanks! -- Duncan Penfold-Brown, Bonneau Lab -------------------- |
| Salmonella |
 Feb 3 2011, 17:15 Feb 3 2011, 17:15
Пост
#59
|
|
кранчер-новачок    Група: Trusted Members Повідомлень: 38 З нами з: 10-June 10 Користувач №: 1 414 Стать: Чол |
Считать американцам их микробиом. Слишком много чести. Хочу родной кефирчик.
|
| Rilian |
 Sep 27 2011, 11:01 Sep 27 2011, 11:01
Пост
#60
|
 interstellar           Група: Team member Повідомлень: 17 049 З нами з: 22-February 06 З: Торонто Користувач №: 184 Стать: НеСкажу Free-DC_CPID Парк машин: ноут и кусок сервера |
Summary The Human Proteome Folding project researchers have published a paper in the journal Genome Research, which announces the availability of their data base of predicted protein structures, their validation methods and how this augments other information about these proteins, thus helping to solve a critical problem for biologists. QUOTE Проект HPF опубликовал статью в Genome Research. Анонсируют доступность их базы данных предсказанных белковых структур, их методы валидации, как новые знания расширяют уже известные знания о данных белках, позволяя решать критические проблемы для биологов. Lay Person Abstract: Lack of information about the structure of proteins is a critical problem for biologists and severely limits their ability to do further research and conduct experiments to understand the roles of proteins in disease processes. The researchers for the Human Proteome Projects have published a paper in Genome Research entitled "The proteome folding project: proteome-scale prediction of structure and function." The paper describes how they were able to use the computation results from World Community Grid to predict protein structure and protein function. Protein structure determines the function of proteins in life processes. Knowing the structure of these proteins helps scientists studying biological and medical processes and can, for example, hasten the process of discovering treatments for diseases. The human genome as well as 93 other genomes of importance to humans were processed. The paper describes the methods used to validate the accuracy of their predictions, which are now publicly available in a data base for all scientists to use. Technical Abstract: The incompleteness of proteome structure and function annotation is a critical problem for biologists and, in particular, severely limits interpretation of high-throughput and next-generation experiments. We have developed a proteome annotation pipeline based on structure prediction, where function and structure annotations are generated using an integration of sequence comparison, fold recognition, and grid-computing-enabled de novo structure prediction. We predict protein domain boundaries and three-dimensional (3D) structures for protein domains from 94 genomes (including human, Arabidopsis, rice, mouse, fly, yeast, Escherichia coli, and worm). De novo structure predictions were distributed on a grid of more than 1.5 million CPUs worldwide (World Community Grid). We generated significant numbers of new confident fold annotations (9% of domains that are otherwise unannotated in these genomes). We demonstrate that predicted structures can be combined with annotations from the Gene Ontology database to predict new and more specific molecular functions. Access to Paper: To view the paper, please click here. -------------------- |
  |
5 Користувачів переглядають дану тему (5 Гостей і 0 Прихованих Користувачів)
0 Користувачів:

|
Lo-Fi Версія | Поточний час: 24th September 2024 - 08:06 |